PacBio anunció una actualización de DeepConsensus, un modelo desarrollado con Google AI Genomics para mejorar la precisión de la secuenciación genómica HiFi. La novedad es que parte de la mejora fue optimizada por AlphaEvolve, el agente de DeepMind basado en Gemini.
PacBio anunció una actualización de DeepConsensus, el modelo de aprendizaje profundo desarrollado junto con Google AI Genomics para mejorar la precisión de las lecturas genómicas HiFi en sus sistemas Revio. La compañía señaló que los avances incorporan aportes de AlphaEvolve, el agente de Google DeepMind diseñado para descubrir y optimizar algoritmos mediante modelos Gemini y evaluadores automatizados.
La secuenciación genómica HiFi es una tecnología que permite leer fragmentos largos de ADN con alta precisión. Para lograrlo, el sistema observa varias veces la misma molécula y construye una secuencia de consenso, reduciendo errores de lectura.
El ADN es como un texto larguísimo escrito con cuatro letras químicas A, C, G y T. Secuenciar significa leer el orden de esas letras. La tecnología HiFi, de PacBio, intenta hacerlo generando lecturas largas y muy precisas.
La gracia de HiFi es que no lee una sola vez el fragmento de ADN. Lo lee varias veces, como si pasaras varias veces por la misma frase borrosa, y luego construye una versión de consenso. Por eso se llaman lecturas HiFi, de “high fidelity”: alta fidelidad.
La actualización forma parte de una mejora más amplia para la plataforma Revio, prevista para mediados de 2026 y disponible ya en algunos sitios seleccionados. Según PacBio, el paquete incluye nuevas celdas SMRT multiuso, química SPRQ-Nx y cambios de software que buscan reducir el costo de secuenciar un genoma humano HiFi a alrededor de 345 dólares.
Esto no significa que cualquier rastro de ADN pueda convertirse hoy, de manera inmediata, en una identidad personal. La identificación genética depende de la calidad de la muestra, la cantidad de material disponible, las bases de datos de comparación, los métodos de análisis y el marco legal. Pero el anuncio de PacBio y Google apunta a una tendencia más amplia: reducir el costo técnico de leer lo biológico.
El punto más relevante no está solo en la reducción de costos, sino en el tipo de intervención tecnológica que describe el anuncio: una IA, AlphaEvolve, fue utilizada para mejorar componentes de otra IA, DeepConsensus, que a su vez participa en el procesamiento de datos genómicos.
DeepConsensus es un modelo basado en transformers que corrige errores en lecturas de secuenciación PacBio. De acuerdo con Google Research, el modelo redujo en 42% los errores en lecturas HiFi frente a métodos previos y aumentó el rendimiento de lecturas de alta calidad en distintos umbrales de precisión.
En los sistemas Revio, DeepConsensus se usa para generar lecturas HiFi a partir de observaciones repetidas de una misma molécula de ADN. PacBio explica que la técnica permite construir una secuencia de consenso más precisa, ya que cada observación individual puede contener errores, pero múltiples pasadas ayudan a corregirlos.
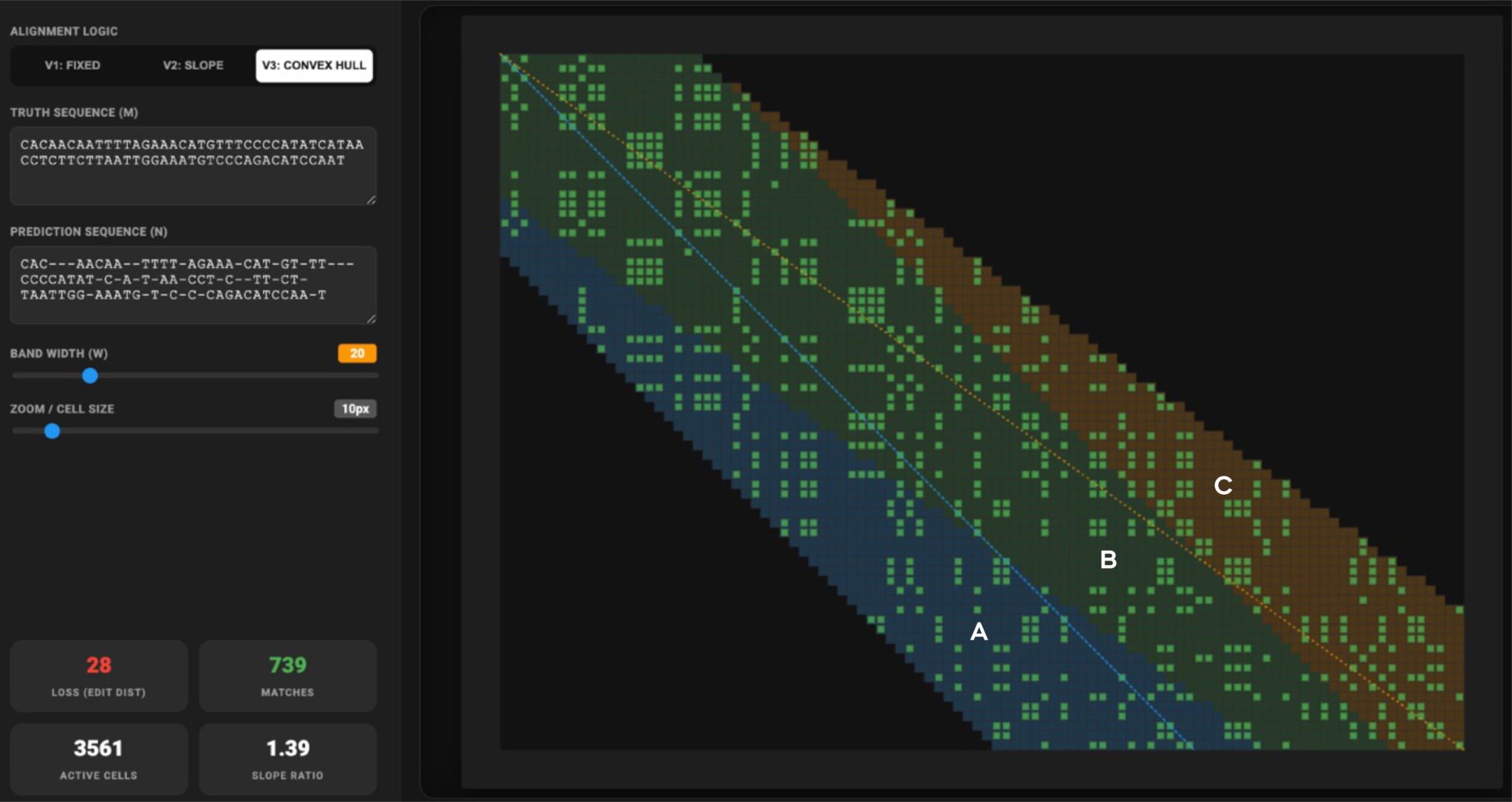
La mejora anunciada ahora se concentra en una parte específica del entrenamiento del modelo: la función de pérdida, es decir, el mecanismo que permite medir qué tanto se alejan las predicciones del modelo respecto de las respuestas correctas. En DeepConsensus, esa función incorpora principios de alineamiento de secuencias de ADN para manejar mejor errores de inserción y eliminación.
Según PacBio, el equipo de Google usó AlphaEvolve para revisar y optimizar componentes de alineamiento que ya existían en el código, pero que no habían mostrado mejoras medibles en experimentos anteriores. Con ayuda del agente, el equipo refinó la implementación y los parámetros, y posteriormente extendió el método con Gemini mediante una modificación denominada “convex hull”.
El resultado, de acuerdo con la compañía, fue la integración de una versión actualizada de AlignmentLoss en los sistemas Revio. PacBio afirma que el cambio elevó el porcentaje de lecturas que alcanzan precisión empírica Q30 de 47.9% a 53.2%, una mejora de 5.3 puntos porcentuales, además de mejorar la calibración de calidad cerca del umbral Q20 usado en lecturas HiFi.
AlphaEvolve fue presentado por Google DeepMind en mayo de 2025 como un agente de codificación para el descubrimiento y optimización de algoritmos. El sistema combina modelos Gemini con evaluadores automatizados que verifican y puntúan las soluciones propuestas, lo que permite aplicarlo en problemas donde el avance puede medirse de forma objetiva.
Google DeepMind ha descrito a AlphaEvolve como una herramienta con aplicaciones en matemáticas, infraestructura computacional, diseño de chips y entrenamiento de modelos de IA. En este caso, su uso aparece dentro de un flujo de trabajo científico y comercial: mejorar los algoritmos que procesan datos de secuenciación genómica.
La noticia muestra una nueva capa en la relación entre IA y biotecnología. No se trata únicamente de usar modelos para interpretar datos biológicos, sino de emplear sistemas de IA para modificar los algoritmos que producen datos biológicos más precisos. PacBio lo presenta como un “bucle” en el que mejores datos permiten entrenar mejores modelos, y mejores modelos ayudan a generar datos de mayor calidad.
El avance no significa que una IA esté “descifrando” por sí sola el genoma humano ni que estos sistemas estén destinados directamente al diagnóstico médico. El propio repositorio de DeepConsensus advierte que el software no está pensado como dispositivo médico ni para uso clínico en diagnóstico o pronóstico.
Aun así, el anuncio ilustra una tendencia inquietante y relevante para la ciencia computacional: la infraestructura que permite leer, corregir y analizar información biológica empieza a depender de modelos capaces de optimizar otros modelos. En la práctica, la genómica entra en una etapa donde la IA no solo interpreta los datos, sino que participa en la construcción de las condiciones técnicas para producirlos.




